—Pareces Neandertal! Suele ser una expresión coloquial para referirse a alguien falto de inteligencia o particularmente primitivo en su comportamiento o aspecto físico. Sin embargo, si tan sólo la gente supiera que decir esto, más que un comentario peyorativo es una reafirmación a nuestra naturaleza, inclusive hasta un cumplido.
El estudio sobre el origen y la evolución humana ha tenido grandes y cruciales avances recientemente. Independientemente de las convicciones religiosas de cada uno, hoy en día existe suficiente evidencia científica como para cuestionarnos, analizar y tratar de empezar a comprender el rompecabezas de nuestro pasado como especie.
Más aún, el estudio de la historia evolutiva humana, se ha visto especialmente enriquecido por dos particulares hitos científicos e impulsados especialmente por los nuevos avances del campo del DNA antiguo. El primero de ellos, es la publicación del primer borrador del genoma del Neandertal, mientras que el segundo es la secuenciación de un homínido desconocido hasta hace recientemente, conocido como “Denisoviano”.
Una de las conclusiones más interesantes que nos ha dejado la publicación de estos genomas homínidos, en especial la del Neandertal, es el hecho de que muy probablemente estos últimos y los humanos no africanos que cohabitaban el planeta en ese momento tuvieron un contacto sexual. Dicho encuentro dejó una huella genética en nuestro genoma, y muy probablemente en el suyo también. Según lo publicado en el 2010 por Green y colegas en la prestigiosa revista científica Science, este acontecimiento posiblemente ocurrió en algún lugar del medio oriente hace ~50,000-60,000 años, mientras el ser humano salía de África durante la migración “Out of Africa” (una de las migraciones en las que el Homo sapiens salió de África y pobló el resto de los continentes). De esta forma aquellos individuos humanos, los cuales tenían la huella de un entrecruzamiento con los Neandertales, transmitieron ésta evidencia a las futuras poblaciones de cuanto territorio poblaron. Según estimaciones hechas por los autores de esta investigación, los humanos no africanos debemos entre un 2-4% de nuestro genoma a los Neandertales. Es decir que, con la excepción de la gente originaria de África, todos somos algo Neandertales después de todo.

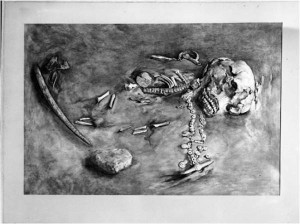
- Reconstrucción artística de la cara de una mujer neandertal basada en datos antropológicos e información genética
Sin embargo, aún quedan muchas preguntas sin responder. Por ejemplo, ¿Todos compartiremos las mismas regiones genéticas de origen Neandertal? ¿Habrá individuos, grupos o poblaciones que tengan más, o menos, de este mestizaje? ¿Si tengo una región de origen Neandertal, ésta está ubicada en algún lugar en especial en mi genoma? ¿Será que alguien tiene un aspecto primitivo porque su DNA tiene más de Neandertal? Esta última pregunta raya un poco en la ciencia ficción y está muy alejada de la realidad, ya que aún estamos muy lejos de encontrar las causas genéticas para muchos rasgos físicos (tamaño, complexión, estructura ósea) u otros, como el comportamiento. No obstante, conocer cuales regiones son de origen Neandertal u de algún homínido antiguo puede ser de mucho interés.
Hace tan sólo un par de semanas, una vez más en la revista Science, Abi-Rached y sus colegas de la Universidad de Stanford, reportaron que algunas de las variantes genéticas del Complejo Mayor de Histocompatibilidad (CMH) eran de origen Denisoviano, el otro homínido antiguo cuyo genoma fue secuenciado el año pasado. El CMH es un grupo de genes cuyos productos participan en la defensa inmunológica del organismo, que es lo que nos protege de enfermedades y organismos patógenos. Esto significa que: ¡parte de la diversidad en estos genes que nos ayudan a contender contra ciertas enfermedades o infecciones se la debemos a estos homínidos!
Sin duda, nuestra naturaleza antropocentrista hace que tendamos a juzgar ciertos rasgos físicos o comportamientos como primitivos, arcaicos, o “menos evolucionados”, solo porque nosotros no los compartimos. No ha pasado mucho tiempo desde que al Neandertal se le consideraba universalmente como un bruto hombre de las cavernas, carroñero, sin imaginación y poca inteligencia que andaba con poca ropa y con un mazo en la mano. Hoy en día sabemos que esta imagen está muy alejada de la realidad. Cada vez son más las evidencias que demuestran que estos “humanos antiguos” enterraban a sus muertos, se pintaban la cara y usaban adornos corporales (lo que habla de una cierta cultura y concepto de divinidad), tenían una dieta más parecida a la de un cazador recolector moderno que a la de un carroñero y fabricaban herramientas, entre otras muchas características “humanas”. Y sin embargo, por alguna razón desconocida, se extinguieron hace aproximadamente 30,000 años.
No obstante, una pequeña parte de su legado vive en la mayoría de nosotros, y existe la posibilidad de que con nuevos avances tecnológicos y análisis de nuevas muestras podamos recuperar aún más información y aumentar nuestros conocimientos sobre estos subestimados humanoides, los cuales aún tienen mucho que enseñarnos, especialmente de nosotros mismos. Quizá sea prudente reflexionar sobre qué adjetivo utilizar la próxima vez que veas a alguien con algún parecido particular o cuando alguien se te cierre en el periférico, ya que puede ser tu primo!
Quisiera terminar invitándolos a complementar este breve relato sobre la historia de nuestra especie y la de los Neandertales con un par de videos muy interesantes. Bajo estas líneas podrán encontrar los links a dos fragmentos de documentales (uno español y otro en inglés) que mediante imágenes, video y entrevistas hace que la narración de este tema sea más interesante y apasionante a la vez.
Hasta la próxima, mi muy probable “lector Neandertal”.
“El genoma Neandertal”
[youtube width="400" height="300" clipid="1socwnkbN5Y" autoplay="0" controls="1" loop="0" disablekb="0" hd="0" showinfo="1" showsearch="0"]
“The Neandertal in us” (da click para ver en You Tube)
Acerca del autor:
Federico Sánchez Quinto es egresado de la UNAM, acualmente estudia un doctorado en Biomédicina, trabajando con DNA antiguo y evolución genética humana en la Universitat Pomepu Fabra, en Barcelona, España.
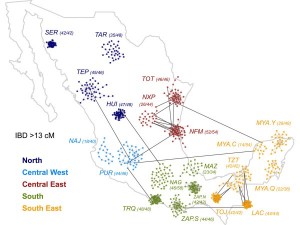 Si pensamos en los rasgos entre un japonés y un alemán, podremos darnos una idea de lo distintos que son sus genomas. De este tamaño es la diferencia a nivel genético entre los mexicanos.
Si pensamos en los rasgos entre un japonés y un alemán, podremos darnos una idea de lo distintos que son sus genomas. De este tamaño es la diferencia a nivel genético entre los mexicanos.